一直以来,从阅读文献中析出可行的Protocol并不是一件简单的事情,希望这篇文章能够给大家带来一些新的思路。本文将介绍一种基于Matlab实现的神经影像与脑电数据融合分析方法,该方法于2018年发表在Nature Protocols杂志上,题目为:Integrated analysis of anatomical and electrophysiological human intracranial data,作者为加州大学伯克利分校Helen Wills神经科学研究所的Arjen Stolk等人。

1 概述
颅内脑电图(intracranial electro-encephalogram,iEEG)是指植入颅内的电直接记录得到的脑电数据。根据电极放置位置可将iEEG分为两大类,一类是将电极放置在大脑皮层的皮层脑电图(electrocorticography,ECoG),另一类是将电极放置在脑深部组织的立体定向脑电图(stereoelectroencephalography,SEEG)。在神经电生理数据记录中,与头皮脑电图(electroencephalogram,EEG)、脑磁图(Magnetoencephalography,MEG)或功能性磁共振(functional magnetic resonance imaging,fMRI)相比,iEEG具有更高的时空精度,对科学研究具有重要意义。
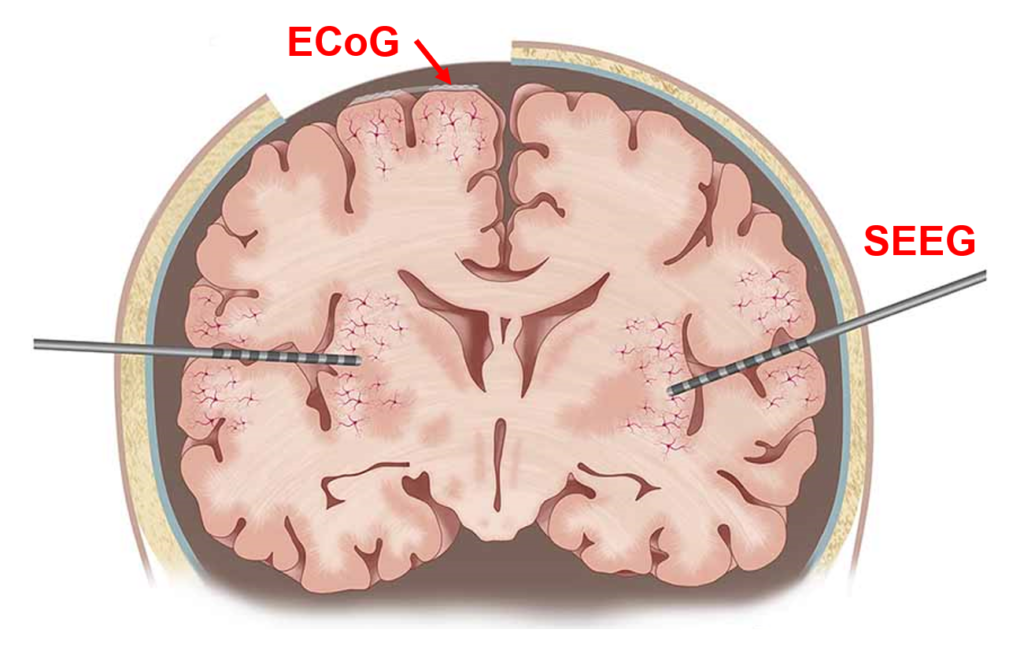
(a)ECoG和SEEG1
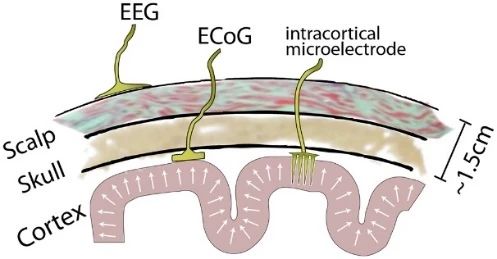
(b)ECoG和EEG 2图1 不同神经电生理数据记录方式
由于外科手术中植入电极的实际解剖学位置需要依靠术前术后的神经影像检查(主要为MRI和CT)来确定,因此影像数据处理是iEEG数据分析的必要步骤。此前,研究人员往往需要使用不同软件的组合来完成影像文件格式转换、影像配准、电极定位等多项解剖数据的处理,同时需要对解剖图像中的电极进行排序与标记以匹配iEEG数据格式,然后再进行电生理数据分析,工作繁琐且缺乏规范流程。在这篇文献中,作者提出了一个完整的分析方法,能够在单个工作环境(Matlab)中完成影像数据的全部处理,并支持后续的电生理数据分析,操作过程透明,具有较高的自动化程度、可重复性与适应性。
另一方面,对于电生理数据,研究人员的分析往往涉及多个维度,例如,原始神经信号具有两个维度(通道和时间),而时频分析将产生三个维度(功率与通道、时间和频率的函数关系),进一步的通道间连接分析则会将其扩展到四个维度,这使得数据的整体可解释性大复杂化。针对电生理数据的多维度特点,该方法实现了对iEEG的多维可视化表示。该方法生成的交互式界面支持研究人员查看特定数据在不同维度的可视化表示,并相互关联,很大程度提高了数据的可读性。该方法基于Matlab平台实现,并集成了基于Matlab的开源工具箱FieldTrip,同时可选择性地使用免费软件FreeSurfer用于皮质表面提取。在不包括皮质表面提取的情况下,执行全部流程大约需要一个小时。
2 主要工作流程
该方法共包含3个部分(图2):解剖学(影像)数据处理、功能学(脑电)数据处理以及可视化表示。其中影像数据和脑电数据可并行处理,最后进行脑电数据在影像上的可视化表示。影像数据处理过程包含电极的定位,这一步骤将把解剖学数据和功能学数据联系起来。以下说明将介绍该方法的主要工作流程,其中包含部分可选操作(如使用FreeSurfer提取皮质表面等),展示的结果基于这篇文献提供的示例代码和示例数据集。
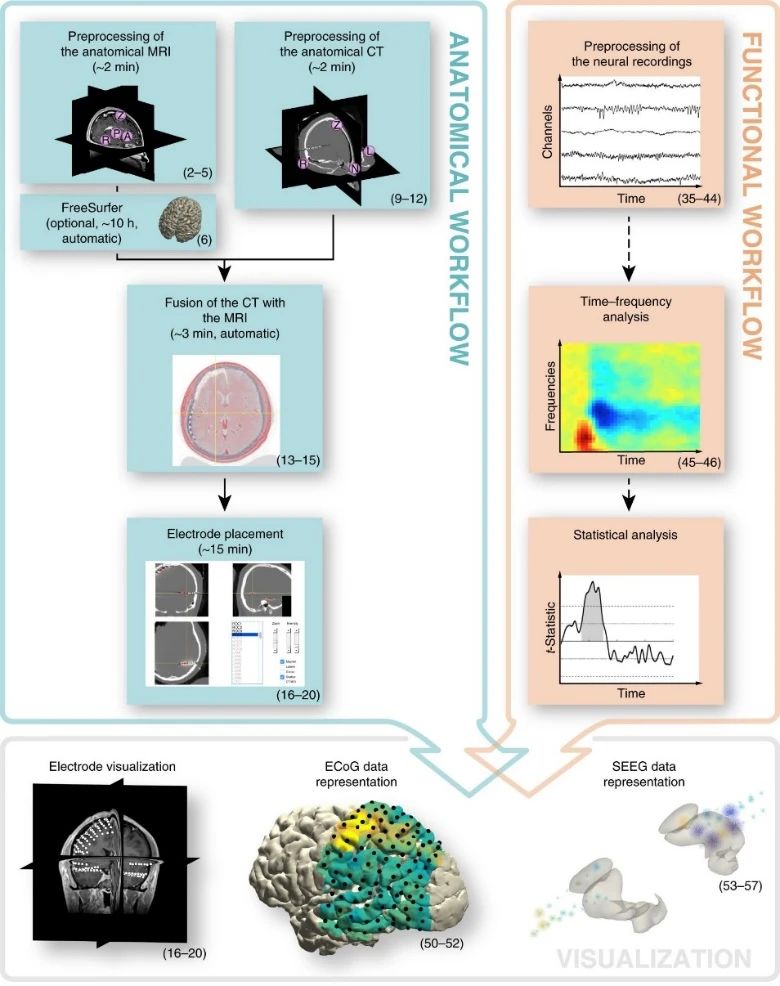
图2 工作流程(原文Fig. 1)
1)解剖学(影像)数据处理
·MRI(植入电极前)数据处理
MRI数据的处理主要包括数据格式的转换以及坐标系的确定。在该方法中,MRI数据的读入支持扩展名为 .img 或 .nii 的单个文件,或包含一系列扩展名为 .dcm 或 .ima 的文件的文件夹。读入MRI文件后,根据生成图像(图3a)在命令窗口选择MRI左右轴的原生方向。
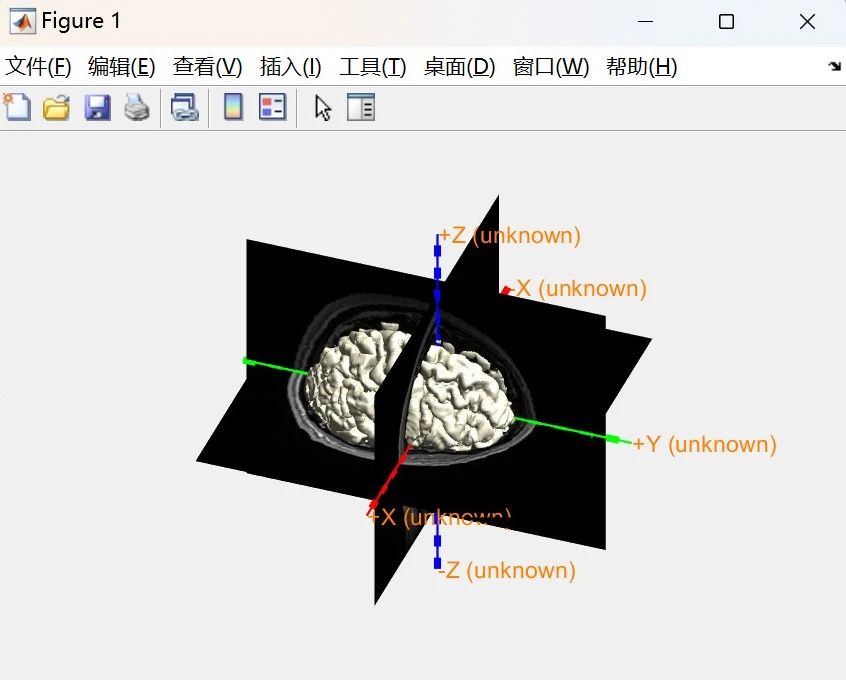
(a)
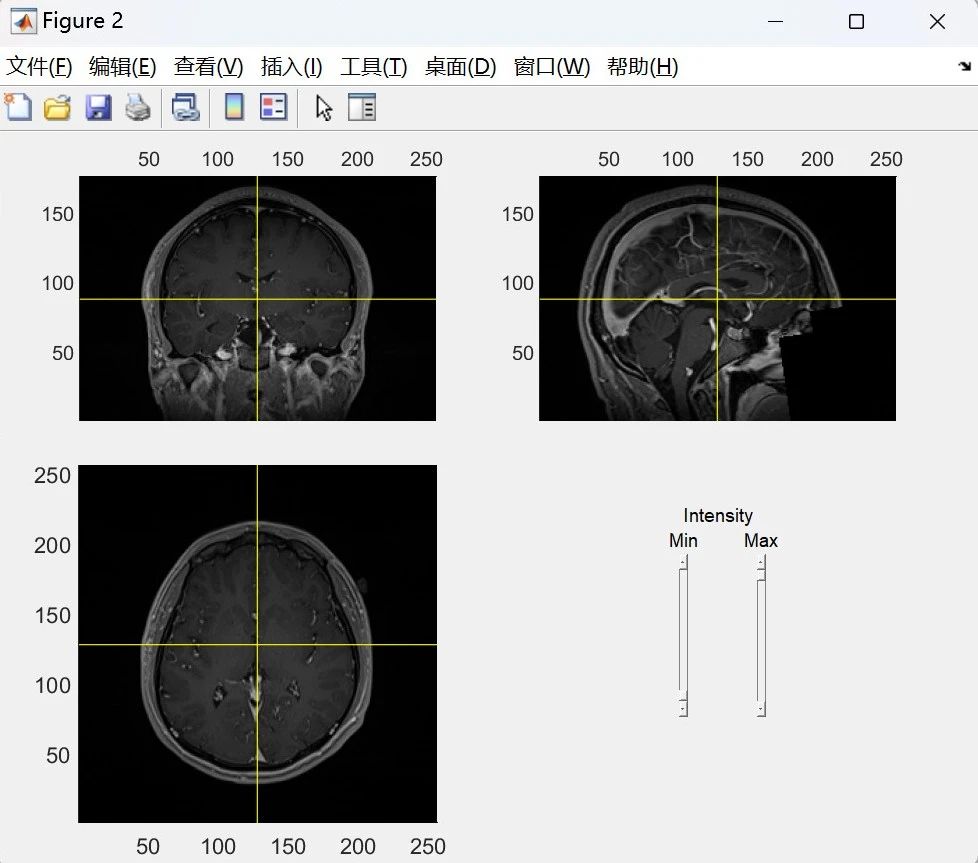
(b)图3 MRI数据处理界面接下来,需要将MRI与ACPC坐标系对齐。ACPC坐标系是指以前连合(anterior commissure,AC)与后连合(posterior commissure,PC)的连线(AC-PC线)为基准所建立的坐标系(图4),在这个坐标系中,原点位于AC处,y轴沿着AC-PC线延伸,z轴位于分隔两个大脑半球的中线上。根据生成的交互式界面(图3b),研究人员需要做的是指定AC和PC、沿大脑顶部中线的半球间位置以及大脑右半球中的位置。
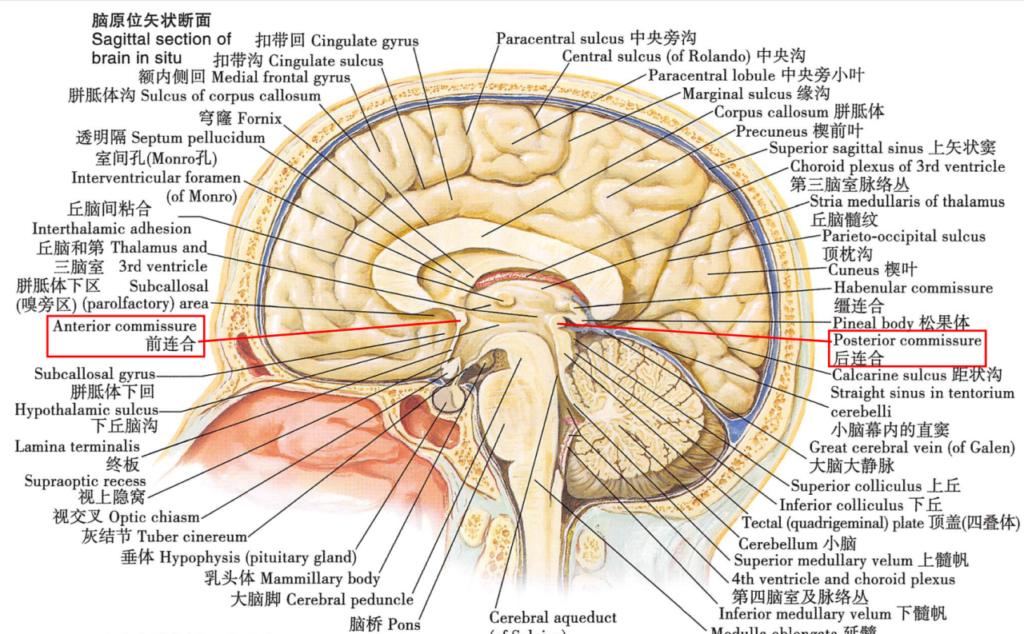
图4 前连合与后连合3对于MRI数据,还可以选择性地使用FreeSurfer进行皮质表面提取。FreeSurfer的核心命令是recon-all,“recon”是reconstruction的缩写,其含义为“重建”,在这里指将三维MRI数据重建为光滑、连续的二维皮质表面。可以理解为对揉成团的纸袋吹气,使其像气球一样膨胀4。该文献提供了在Matlab环境中调用FreeSurfer并执行recon-all命令的代码。
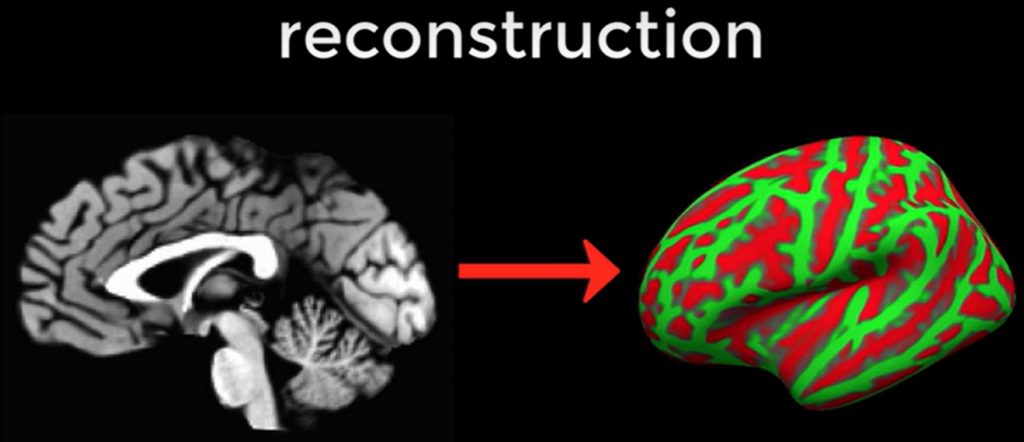
图5 皮质重建4
·CT(植入电极后)数据处理
与MRI类似,CT数据的读入同样支持扩展名为 .img 或 .nii 的单个文件,或包含一系列扩展名为 .dcm 或 .ima 的文件的文件夹。读入CT文件后,根据生成图像(图6a)在命令窗口选择CT左右轴的原生方向。
(a)
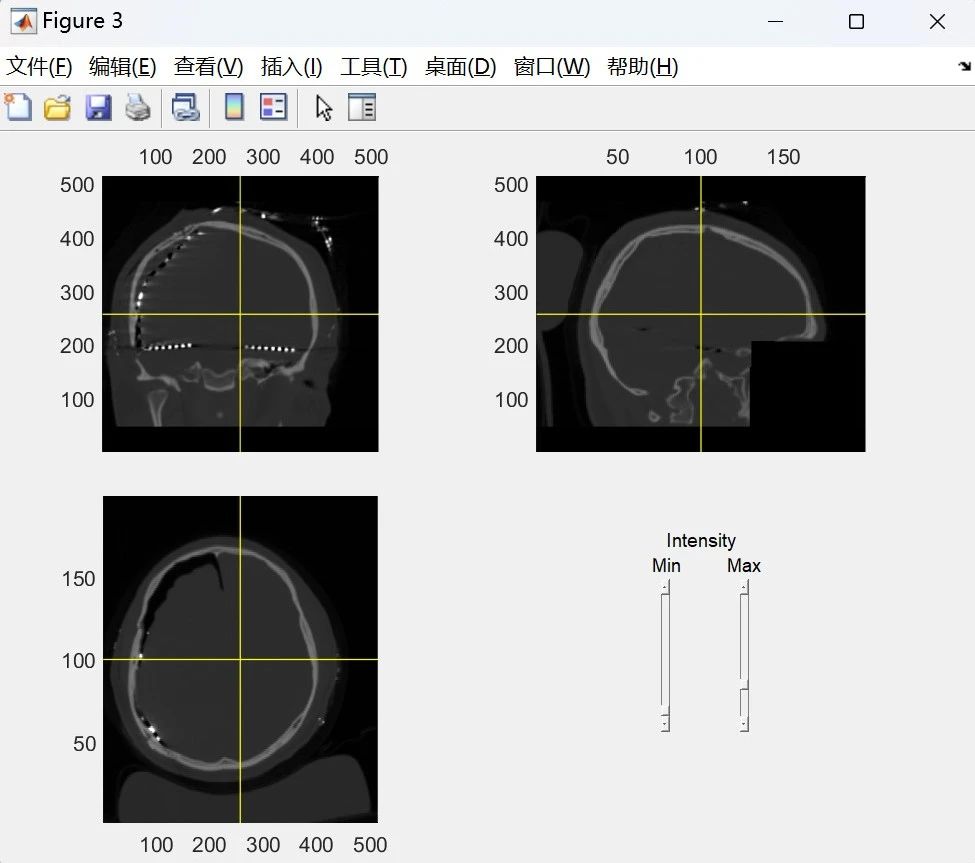
(b)图6 CT数据处理界面
由于ACPC坐标系依赖的神经解剖标志在CT中不可见,因此CT需要先与CTF坐标系对齐。CTF坐标系由鼻根(nasion,NAS)、左耳前点(left pre-auricular point,LPA)和右耳前点(right pre-auricular point,RPA)确定,其原点位于LPA和RPA连线的中点,x轴由原点向NAS延伸,y轴由原点向LPA延伸(图7)。根据生成的交互式界面(图6b),研究人员需要指定鼻根点、左右耳前点和沿大脑顶部中线的半球间位置。接下来,使用FieldTrip的坐标系转换命令自动将CT的坐标系转换为ACPC坐标系的近似值。
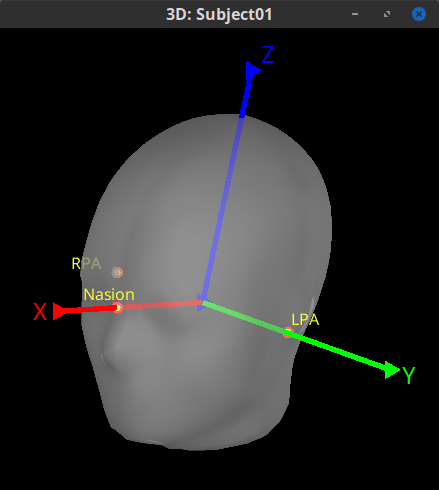
图7 CTF坐标系5
· 影像融合与电极定位
以头骨为参考基准,通过刚体变换将CT与MRI配准。生成的融合图像如图8a所示,其中CT提供颅骨数据(显示为蓝色),MRI提供脑部和皮肤组织数据(显示为红色)。接下来,在交互式图像(图8b)中进行电极定位。该界面可在配准的 CT 和 MRI 视图之间切换,因此可以根据MRI显示的解剖位置识别CT中的特定电极。
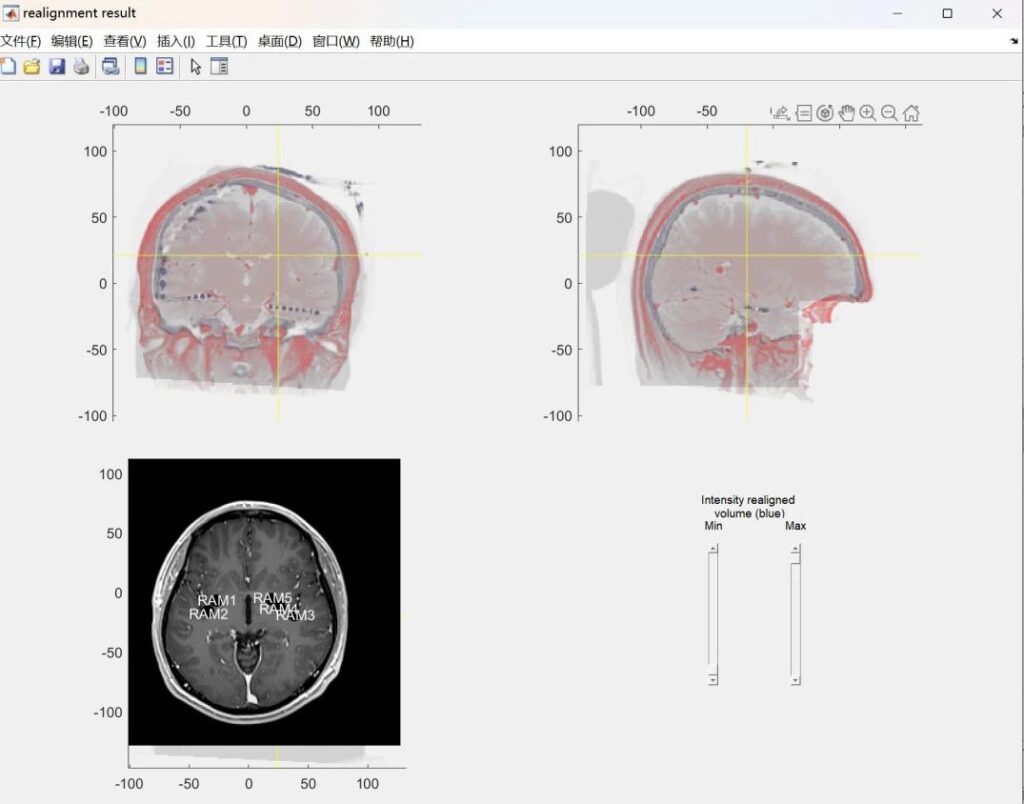
(a)CT与MRI融合图像
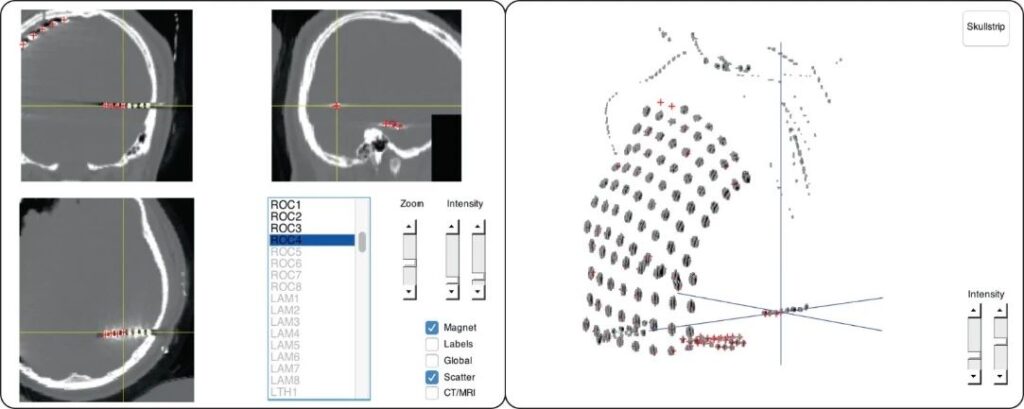
(b)电极定位界面(原文Fig. 2)
图8 影像融合与电极定位
由于开颅手术产生的压力变化可能导致脑组织和电极移位,因此可以选择性地对脑位移”进行补偿。该方法在首先FreeSurfer提取的皮质网格周围创建一个光滑外壳,以跟踪皮质网格的外表面,防止电极被错误地放置在皮质沟中,然后将电极网格重新投影到植入电极前的皮质表面,从而完成脑位移补偿(图9)。
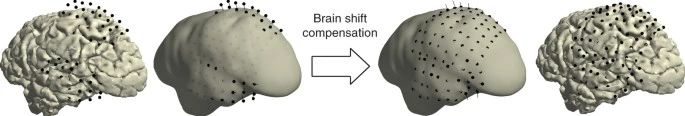
图9 脑位移补偿(原文Fig. 3)
为了便于推广和比较,还可以将电极坐标配准到标准脑图谱。MNI空间(图10a)是一个通过采集大量正常被试的MRI图像后平均得到的标准脑模板,由加拿大蒙特利尔神经研究所(Montreal Neurological Institute,MNI)首先建立。目前广泛使用的标准MNI模板是国际脑图谱联盟(International Consortium for Brain Mapping)所采用的ICBM1526。在MNI空间中,可以基于体积对电极坐标进行配准(图10c),适用于所有类型电极的空间归一化。除此之外,针对位于皮质表面或附近的电极,还可以使用FreeSurfer的fsaverage模板(图10b)基于表面进行配准(图10c)。
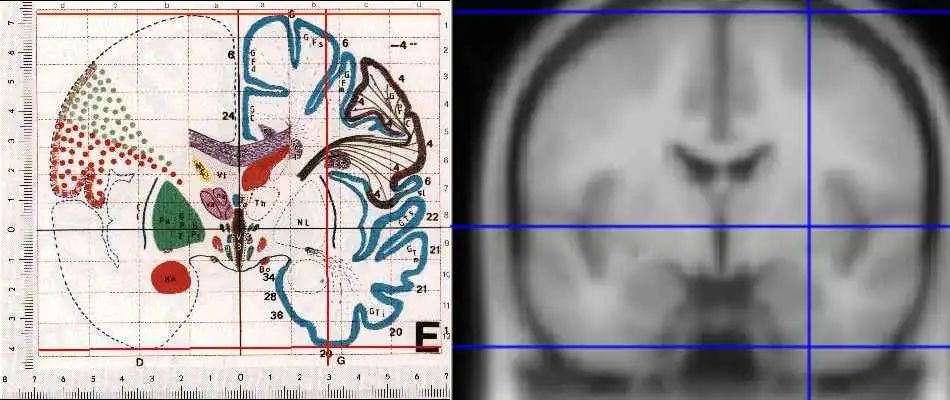
(a)MNI标准空间6

(b)fsaverage模板4
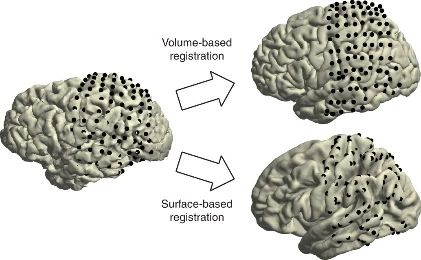
(c)两种配准方法(原文Fig. 4)图10 电极坐标配准到标准空间
2)功能学(电生理)数据处理
电生理数据的预处理主要为伪影剔除。图11所示的交互式界面将iEEG数据以2种模式进行显示,可选择特定通道和时段进行查看。研究人员需要根据命令窗口的提示对脑电数据进行检查和伪影剔除。
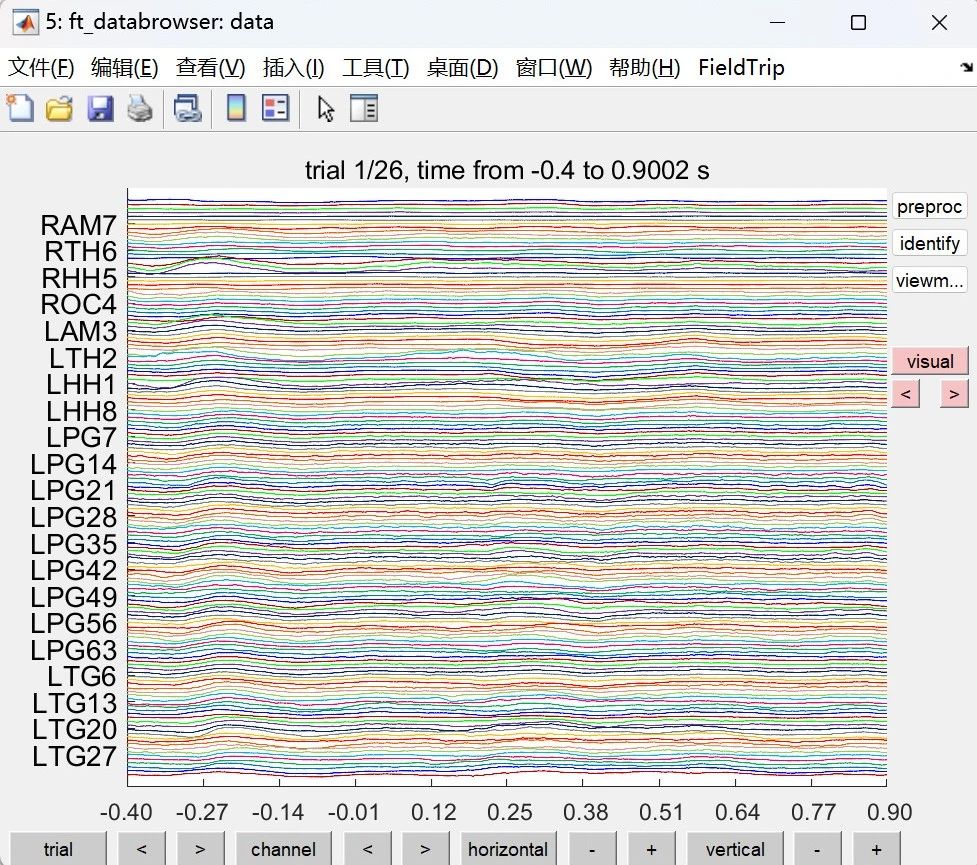
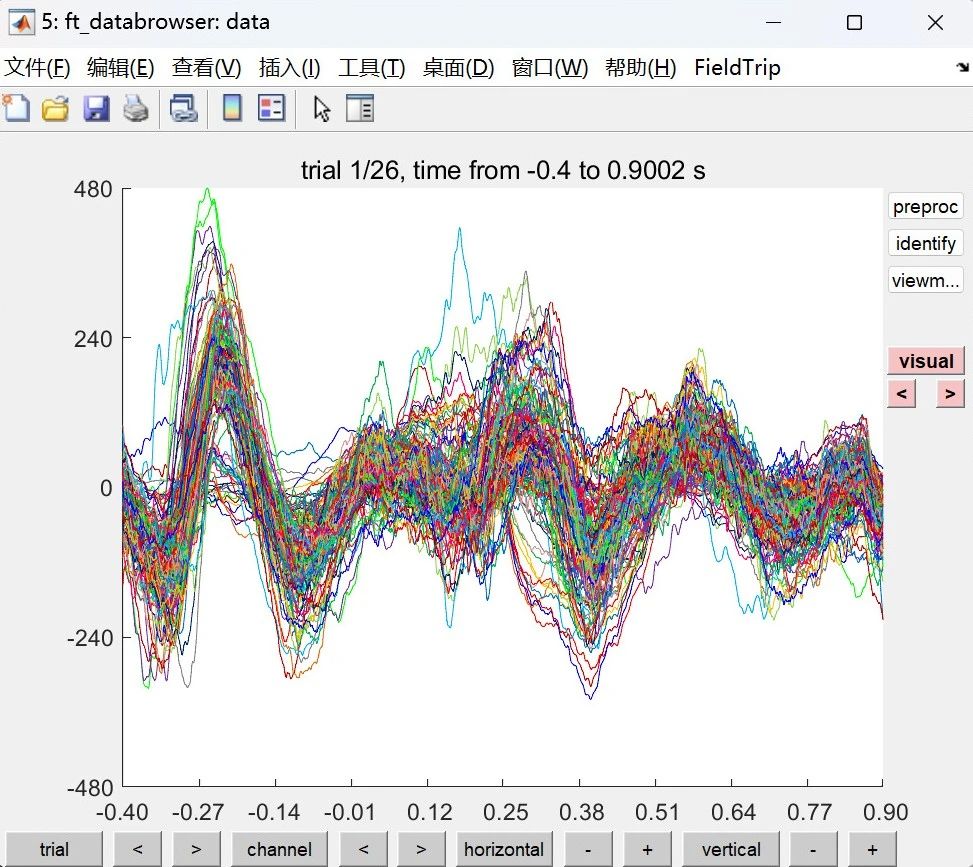
图11 电生理数据处理界面
3)可视化表示
· 交互式显示
如图12所示,生成的交互界面可切换查看iEEG数据在不同维度的可视化表示:首先生成左侧主图,在主图中选择一组信道将启动中间的图,展示这些信道的平均时间-频率图像,在该时频图像中选择某个频率和时间范围则将启动最右侧图,显示所选区间内相应电活动的空间分布,依此类推。
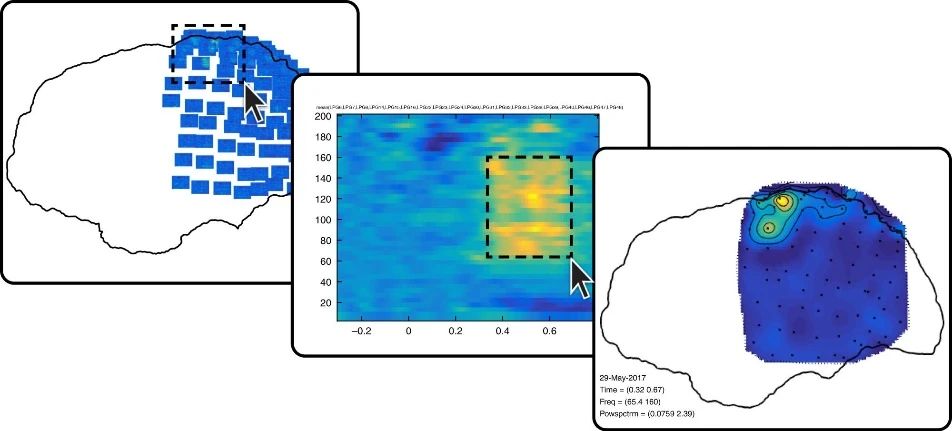
图12 交互式显示(原文Fig. 5)
· ECoG和SEEG数据表示
对于ECoG数据,根据研究需求设置感兴趣的频带和时段,可以生成皮层活动的图像表示,该图像将高频带活动的空间分布与大脑皮质的表面模型叠加在一起,从而在解剖学上真实地表示皮层活动(图13a)。对于SEEG数据,根据研究需求设置感兴趣的频带、时段以及具体核团(区域),可以生成该区域电活动的3D以及2D切片表示。如图13b所示,左侧图像展示了杏仁核和海马体区域高频带活动(70–150 Hz)的3D分布,右侧的图像为左侧图像中黑线指示区域的2D切片。
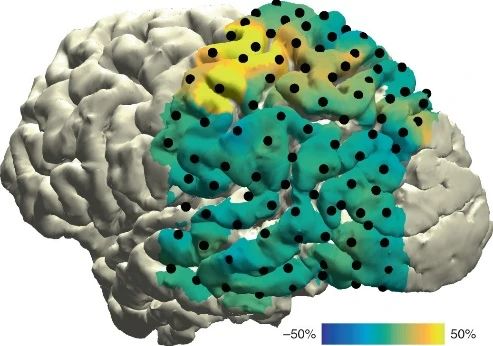
(a)EcoG数据表示(原文Fig. 6)
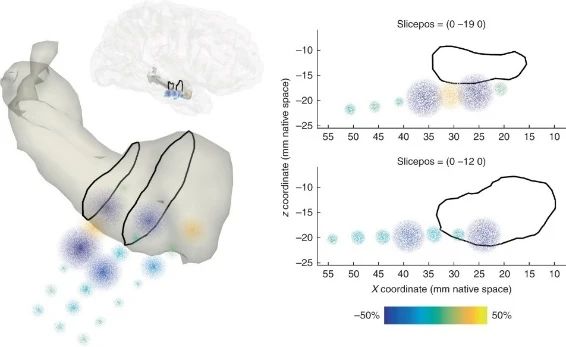
(b)SEEG数据表示(原文Fig. 7)
图13 iEEG数据表示
3 总结
这篇文献发表前,作者所在团队已将其用于对情绪和语言相关的神经动力学和人类海马体的连接性进行研究7,8。该方法自发表至今一直得到广泛应用,一方面是由于其很好地实现了不同软件和功能的集成,具有较高的自动化程度和适应性,另一方面也是由于它为研究人员提供了一个完整的范本,即使是缺少经验的研究生也可以基于此完成全过程的颅内数据处理。此外,比起图形用户界面,这种基于代码的数据处理方法使得整个流程透明化,也更便于研究人员深入了解底层算法原理。
4 【参考文献】
1.Grande, K.M., Ihnen, S.K.Z., and Arya, R. (2020). Electrical Stimulation Mapping of Brain Function: A Comparison of Subdural Electrodes and Stereo-EEG. Frontiers in Human Neuroscience 14. 10.3389/fnhum.2020.611291.
2.Miller, K.J., Hermes, D., and Staff, N.P. (2020). The current state of electrocorticography-based brain–computer interfaces. Neurosurgical Focus FOC 49, E2. https://doi.org/10.3171/2020.4.FOCUS20185.
3.Netter, F.H. (2015). 奈特人体解剖学彩色图谱.
4.Andy’s Brain Book.
5.https://neuroimage.usc.edu/brainstorm/CoordinateSystems.
6.https://imaging.mrc-cbu.cam.ac.uk/imaging/MniTalairach.
7.Zheng, J., Anderson, K.L., Leal, S.L., Shestyuk, A., Gulsen, G., Mnatsakanyan, L., Vadera, S., Hsu, F.P.K., Yassa, M.A., Knight, R.T., and Lin, J.J. (2017). Amygdala-hippocampal dynamics during salient information processing. Nature Communications 8, 14413. 10.1038/ncomms14413.
8.Piai, V., Anderson, K.L., Lin, J.J., Dewar, C., Parvizi, J., Dronkers, N.F., and Knight, R.T. (2016). Direct brain recordings reveal hippocampal rhythm underpinnings of language processing. Proceedings of the National Academy of Sciences 113, 11366-11371. 10.1073/pnas.1603312113.
本文作者:林琪璇 吕鑫
上海交通大学医学院附属瑞金医院 功能神经外科

发表回复